Etiquetas
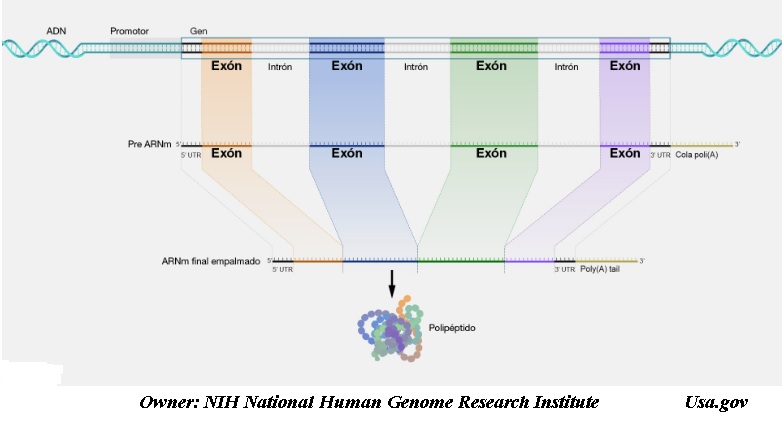
Los genes del genoma consisten en intrones y exones. En 1977 e independientemente el uno del otro, Richard Roberts y Phillip Sharp demostraron cómo el ARN se puede dividir en intrones y exones, después de lo cual los exones se pueden unir.
El dogma central de la genética: el ADN se transcribe en ARN para su traducción en proteínas.
La transcripción de un gen a ADN, genera un ARN mensajero inmaduro.
1º Este ARN mensajero tiene que ajustarse: se eliminan los intrones y las regiones no traducidas, los intrones no codifican ninguna proteína y se eliminan del ARNm.
2º Una vez que el ARN mensajero ha madurado, se traduce a una proteína.
Los intrones son trozos muy grandes de ARN dentro de una molécula de ARN mensajero que interfieren con el código de los exones. Estos intrones se eliminan de la molécula de ARN (para dejar una serie de exones unidos entre sí) de manera que se puedan codificar los aminoácidos correctos, juegan un papel importante para que éstas se fabriquen de forma correcta.
Un exón es una región del genoma que finaliza con una molécula de ARNm. Algunos exones son codificantes, es decir que contienen información para producir una proteína, mientras que otros no son codificantes.
Los factores que intervienen en la reacción de corte de intrones y empalme de exones del ARN intervienen en la producción de ARNm parcialmente distintos: algunos exones pueden ser eliminados junto con los intrones que los flanquean, se crean diferentes versiones de ARN mensajeros que son traducidas a su vez en diferentes proteínas también funcionales
Bibliografía:
NIH: «Exón»
https://www.genome.gov/es/genetics-glossary/Exon
Bach, Moserrat, «Corte de intrones y empalme de exones», Rev. Investigación y Ciencia, nº 188, Mayo 1992
https://www.investigacionyciencia.es/revistas/investigacion-y-ciencia/pinzamiento-de-membrana-59/corte-de-intrones-y-empalme-de-exones-5206,
Universidad Autónoma de Barcelona. «SPLICING-EXONES E INTRONES2019_4_29P13_10_53.pdf», Bioinformática
http://bioinformatica.uab.cat/base/documents/genetica_gen/portfolio/SPLICING-EXONES%20E%20INTRONES2019_4_29P13_10_53.pdf
Chow, L.T., Roberts, J.M., Lewis, J.B., Broker, T.R. «A map of cytoplasmic RNA transcripts from lytic adenovirus type 2, determined by electron microscopy of RNA:DNA hybrids». Cell, 11(4): 819-36. 1977.
https://pubmed.ncbi.nlm.nih.gov/890740/
Berk, A.J., Sharp, P.A. «Sizing and mapping of early adenovirus mRNAs by gel electrophoresis of S1 endonuclease-digested hybrids». Cell, 12(3): 721-32. 1977.
https://pubmed.ncbi.nlm.nih.gov/922889/
Berget, S.M., Sharp, P.A. «A spliced sequence at the 5′-terminus of adenovirus late mRNA». Brookhaven Symp Biol, 29:332-44, 1977.
https://www.ncbi.nlm.nih.gov/pmc/articles/PMC431482/
